🧠 New comprehensive review on #LowDimensional #embeddings of #HighDimensional data. Discusses how #dimensionalityreduction helps visualizing, exploring, and #modeling #ComplexSystems. From #PCA to #tSNE, #UMAP & #NeuralNetworks: Excellent overview paper👌
#ReleaseTuesday — New version of https://thi.ng/tsne with ~15-20% better performance[1] due to avoiding repeated internal allocations and skipping gradient updates where unnecessary...
[1] Benchmarked with multiple datasets of ~750 items, each with 192 dimensions (now ~165ms @ MBA M1, 2020)...
#ThingUmbrella #TSNE #DataViz #Visualization #ML #Cluster #TypeScript #JavaScript
my #tsne in #futhark (compiled to Python) iteratively spreading 10dimensional-clustered data (easy mode) into 2dimensions
it's not as fast as I hoped. In part because I'm not good at futhark yet, and in part because the Python target may not be optimized, however it's _fun_.
Based on "Visualizing Data using t-SNE" (Laurens van der Maaten and Geoffrey Hinton).
(click or leave your pointer on the image, 1, 5, 10, 15, and 25 iterations)
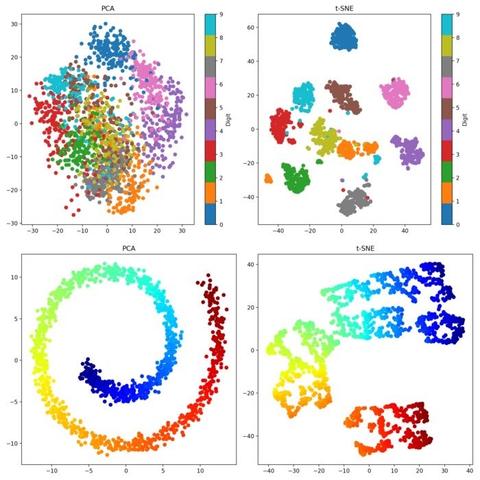
2D embeddings for high-dimensional data, the battle rages on
https://journals.plos.org/ploscompbiol/article?id=10.1371/journal.pcbi.1012403
The art of seeing the elephant in the room: 2D embeddings of single-cell data do make sense
A recent paper claimed that t-SNE and UMAP embeddings of single-cell datasets are “specious” and fail to capture true biological structure. The authors argued that such embeddings are as arbitrary and as misleading as forcing the data into an elephant shape. Here we show that this conclusion was based on inadequate and limited metrics of embedding quality. More appropriate metrics quantifying neighborhood and class preservation reveal the elephant in the room: while t-SNE and UMAP embeddings of single-cell data do not preserve high-dimensional distances, they can nevertheless provide biologically relevant information.
Может ли простейшая нейросеть найти математическую закономерность в данных?
В этой небольшой статье мы научим нейросеть решать задачу умножения перестановок длины 5 (группа ) и визуализируем результаты обучения с помощью методов проекции t-SNE (с понижением размерности PCA) и алгоритма UMAP. Мы убедимся в том, что даже элементарная модель может "неосознанно" провести бинарную классификацию перестановок.
Как анализировать тысячи отзывов с ChatGPT? Частые ошибки и пример на реальных данных
В этой статье я расскажу про свой опыт решения рабочей задачи — анализ отзывов о компании от пользователей. Мы разберем возможные ошибки и посмотрим на пример кода и реальных данных. Гайд будет полезен всем, у кого нет большого опыта в анализе данных или работе с LLM через API.
https://habr.com/ru/articles/821287/
#llm #gpt #chatgpt #python #clustering #kmeans #tsne #visualization #summarization #data_analysis
“Biostatistician Rafael Irizarry… dislikes many of the t-SNE and UMAP plots he sees. They offer little of value to a paper, he says, and the output from these tools is analytically intractable.”
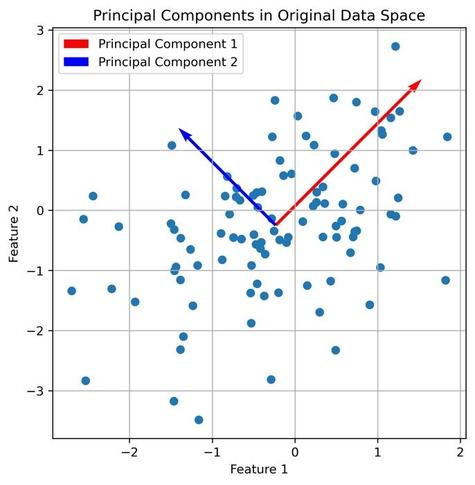
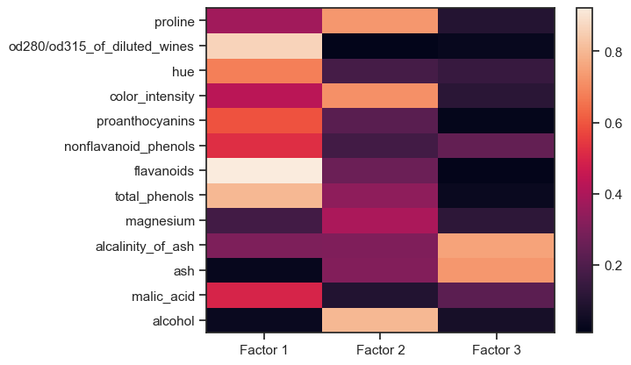
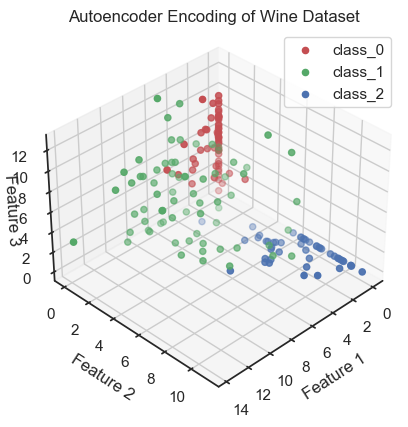
These four #Python #tutorials introduce and discuss #PCA, #tsne, #factoranalysis, and #Autoencoder as powerful tools for #DimensionalityReduction:
🌍 https://www.fabriziomusacchio.com/blog/2023-06-16-pca_with_python/
🌍 https://www.fabriziomusacchio.com/blog/2023-06-12-tsne_vs_pca/
🌍 https://www.fabriziomusacchio.com/blog/2023-06-16-factoranalysis_with_python/
🌍 https://www.fabriziomusacchio.com/blog/2023-06-16-autoencoder_with_python/
Feel free to share, use and remix 😊🙏
Untangling complexity: harnessing PCA for data dimensionality reduction
This tutorial explores the use of Principal Component Analysis (PCA), a powerful tool for reducing the complexity of high-dimensional data. By delving into both the theoretical underpinnings and practical Python applications, we illuminate how PCA can reveal hidden structures within data and make it more manageable for analysis.
The difference between mapping an n-dimensional feature space to three or two dimensions.