В 2025 году китайские исследователи представили Difface — революционную систему, способную воссоздавать 3D-модель лица человека исключительно по его ДНК. Используя данные о вариациях в генах (SNP), алгоритм предсказывает анатомические черты — форму носа, скул, подбородка и другие элементы внешности. Впервые биоинформатика и компьютерное зрение достигли такой точности, что становится возможным идентифицировать личность даже без фото или свидетельских показаний. Эта технология открывает новую эпоху в криминалистике, медицине и биометрии — но вместе с тем несёт экзистенциальные риски тотального контроля над телом, данными и личной свободой.
Пул учеников мединских соотоварищи заревом огня пуканов:
"Китайские учёные создали программу Difface: ИИ по ДНК может воссоздать 3D-модель лица человека. Анализируются гены (SNP — небольшие вариации в ДНК), влияющие на форму носа, линию скул, подбородок и др. черты. Если ввести данные о возрасте, поле и индексе массы тела, можно спрогнозировать, как лицо будет меняться с годами. Алгоритм построен на базе данных 9674 добровольцев, которые предоставили полную последовательность своего генома ДНК и 3D-сканы лица высокого разрешения. Результаты хорошие, все черты удалось воссоздать с точностью. Возможное применение: -- криминалистика. Создание портретов подозреваемых по найденной ДНК, даже при отсутствии свидетелей или видеозаписей (данные могут быть получены из одного волоса или капли слюны); -- медицина. Диагностика генетических заболеваний и предсказания возрастных изменений; --генетика и биометрия. Новые методы идентификации и анализа наследуемых признаков.
… всё идёт по одному сценарию, к уничтожению остатков разума, воли и свободы как таковых. Это и есть конец классической истории человечества. Никакого «дальше» не будет."
Штош, опишем не для аутистов и (или) бабок из отрядов путена:
**Difface: Воссоздание лица по ДНК с помощью искусственного интеллекта**
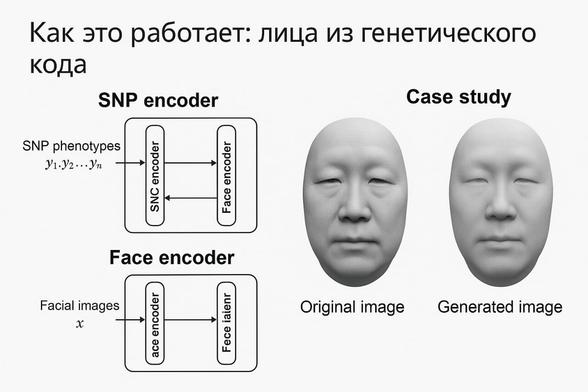
В 2025 году исследователи из Китая представили Difface — модель машинного обучения, способную по данным ДНК реконструировать трёхмерную модель человеческого лица. Разработка основана на глубоком обучении и обрабатывает однонуклеотидные полиморфизмы (SNP), сопоставляя их с геометрией лицевых черт.
Методология
Модель обучена на базе данных из 9674 добровольцев, каждый из которых предоставил полную последовательность генома и 3D-скан лица высокого разрешения. Архитектура Difface состоит из двух ключевых компонентов:
**SNP-энкодер**: преобразует генетические признаки (SNP-фенотипы) в латентное представление с использованием трансформеров и MLP.
**Face-энкодер**: аналогично кодирует 3D-изображения лиц в латентное пространство с помощью сверточных сетей на спиральной топологии (SpiralConv).
Совпадение между этими пространствами позволяет осуществлять точную реконструкцию: при наличии только ДНК Difface генерирует лицо, приближенное к реальному.
Результаты
Тестирование модели показало высокую точность в восстановлении ключевых анатомических черт, таких как:
носовая проекция;
ширина скул;
контуры челюсти и подбородка;
выраженность надбровных дуг.
Точность повышается при добавлении таких параметров, как возраст, пол и индекс массы тела, которые также влияют на морфологию.
Потенциальные области применения
**Криминалистика**: реконструкция внешности по генетическим следам (волосы, слюна) при отсутствии фотографий или свидетелей.
**Генетическая диагностика**: предсказание дисморфий, связанных с наследственными заболеваниями.
**Биометрия и идентификация**: создание дополнительных методов аутентификации и анализа родственных связей.
Ограничения
Точность модели ограничена размером и этническим разнообразием обучающей выборки.
Черты лица зависят не только от генома, но и от факторов окружающей среды (эпигенетика, травмы, питание).
Модель не учитывает выражение эмоций или мимику.
Заключение
Difface представляет собой значительный шаг вперёд в области предсказательной геномики и 3D-моделирования. Это первый масштабный пример применения трансформеров и геометрических нейросетей для корреляции между SNP и морфологией лица. Технология демонстрирует потенциал для интеграции в медицинские, судебные и биометрические системы — при соблюдении этических и правовых норм.
🔮** Прогноз:**
Технология Difface знаменует собой поворотный момент в биометрической идентификации и предиктивной медицине. В ближайшие 5–7 років алгоритмы восстановления лица по ДНК станут стандартом в криминалистике и генной диагностике. Однако масштабне впровадження подібних систем може призвести до ерозії приватності: кожна втрата волосини стане актом самовикриття. У синергии з масовим генотипуванням та камерами розпізнавання облич алгоритми на кшталт Difface загрожують злиттям біометричної тиранії й превентивної юриспруденції. Це не розвиток — це досконале стирання людської непередбачуваності.
📚** Библиография:**
Qiao, X. et al. (2024). *Facial shape prediction from genomic data using deep learning*. National Science Review.
Claes, P. et al. (2018). *Modeling 3D Facial Shape from DNA*. PLOS Genetics.
Lippert, C. et al. (2017). *Identification of individuals by trait prediction using whole-genome sequencing data*. PNAS.
Erlich, Y. (2017). *Major flaws in “DNA Face Prediction”*. Nature Blogs.
NIST (2022). *Face Recognition Vendor Test (FRVT) – Biometric Evaluation Reports*.
#Хэштеги:
#Difface #ГенетичнеСканування #ІдентифікаціяПоДНК #Біометрія #КриміналістикаМайбутнього #ГенетичнаПриватність #ЦифровийЛевіафан #КінецьІсторії #AIфорензіка #СинтетичнаАнтропологія #Геноміка2025 #DeepFaceReconstruction #BioSurveillance #Антропоалгоритмізація
Хочете доповнення або стислу англомовну версію — скажіть.
#GenomicAI
#DNAtoFace
#FacialReconstruction
#SNPanalysis
#3DfacePrediction
#ForensicGenomics
#BiometricAI
#GeneticPhenotyping
#DeepLearningGenomics
#AIinForensics
#PredictiveGenomics
#DNAImaging
#FacialBiometrics
#GenomeToGeometry
#PrecisionPhenotyping